¡Tu carrito está actualmente vacío!
Desentrañando la mecano-transcriptómica espacial: una ventana hacia la biología del desarrollo
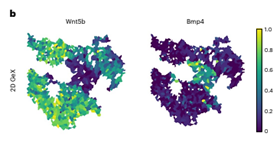
La biología del desarrollo ha sido transformada por las tecnologías de análisis de perfiles espaciales, que permiten mapear la expresión génica en tejidos con resolución celular. Sin embargo, las decisiones de destino celular y la organización tisular no solo dependen de programas moleculares, sino también de fuerzas mecánicas que actúan sobre las células, lo cual es crucial durante el desarrollo. Un estudio reciente publicado en Nature Methods [1] presenta un avance crucial: un marco computacional para integrar señales transcripcionales y mecánicas en un contexto espacial, lo que permite entender cómo ambas dimensiones cooperan para dar forma a los tejidos.

El pipeline desarrollado por Hallou y colaboradores combina imágenes de alta resolución, segmentación celular precisa y modelos estadísticos avanzados para inferir tensiones en las uniones célula-célula y presiones intracelulares a partir de secciones tisulares de embriones de ratón en desarrollo. La innovación clave radica en utilizar métodos de inferencia mecánica basados en la geometría celular y en integrarlos con datos de transcriptómica espacial generados por tecnologías como seqFISH (sequential Fluorescence In Situ Hybridization) una técnica que permite la identificación de miles de moléculas como ARN, ADN y proteínas directamente en células con su contexto espacial preservado (https://github.com/CaiGroup).
Uno de los resultados más impactantes de este trabajo es la identificación de tensiones aumentadas en los límites entre compartimentos tisulares, como entre el mesodermo craneal y el prosencéfalo/mesencéfalo en embriones de ratón. Este patrón de alta tensión interfacial es suficiente para explicar el mantenimiento de límites celulares, como demostraron los autores mediante simulaciones in silico. La mecánica y la biología molecular convergen así para estabilizar la arquitectura de los tejidos.
Para desentrañar los mecanismos moleculares que subyacen a estas diferencias mecánicas, los investigadores realizaron un análisis de interacciones ligando-receptor (LR) en las células situadas en los límites tisulares. Identificaron múltiples pares LR, especialmente de la familia efrina–Eph, que son conocidos por inducir repulsión celular y aumentar la tensión interfacial a través de la activación de vías de contracción actomiosina. Además, observaron perfiles recíprocos de expresión de cadherinas entre tejidos adyacentes, lo cual refuerza la hipótesis de que la adhesión diferencial y la contracción celular coordinada contribuyen al mantenimiento de los límites.
La integración de la mecánica y la transcriptómica no solo revela mecanismos de organización tisular, sino que también permite detectar genes cuya expresión responde de manera sensible a las fuerzas mecánicas. Los autores identificaron más de un centenar de genes asociados a presión y tensión celular, muchos de ellos implicados en migración celular, morfogénesis y organización de la matriz extracelular. Entre estos destacan genes relacionados con la transducción mecano-sensible, como Cav1, Cyr61 y Apba2, que sugieren la existencia de filtros tipo band-pass y band-stop en la regulación génica por fuerzas.
Un aspecto fascinante del estudio es la detección de respuestas no lineales entre la expresión génica y las propiedades mecánicas. Algunos genes se expresan solo dentro de intervalos específicos de presión o tensión, lo que podría representar un mecanismo biológico de sintonización fina, donde ciertas funciones celulares solo se activan en condiciones mecánicas óptimas. Esto abre un nuevo campo para el análisis de expresión génica en el que ya no es el detalle fino del promotor lo que importa, sino el contexto celular y mecánico. Esto se asemeja a comportamientos diseñados en biología sintética, pero aquí se observa en tejidos nativos, lo que abre nuevas preguntas sobre su regulación.
Este marco computacional también incluye modelos estructurales geo-aditivos (gSEM) que controlan por distractores espaciales, permitiendo identificar asociaciones genuinas entre la mecánica y la expresión génica más allá de simples correlaciones debidas a proximidad espacial o tipo celular. Estos modelos robustos son esenciales para explorar cómo la mecánica y los programas moleculares se influyen mutuamente durante la formación de órganos.
Las aplicaciones de este enfoque son vastas: desde la biología del desarrollo y la embriología, hasta el estudio del cáncer, donde las tensiones tisulares anómalas pueden afectar la progresión tumoral y muy probablemente la expresión génica. Además, la posibilidad de inferir estados mecánicos a partir de perfiles de expresión, y viceversa, abre caminos para predecir comportamientos celulares en tejidos sin necesidad de medir directamente la mecánica.
En conclusión, este estudio no solo aporta una herramienta innovadora para la biología computacional, sino que también sienta las bases para un nuevo paradigma en el análisis de datos ómicos: la integración de la información mecánica con la molecular. Este enfoque permitirá a la comunidad científica descubrir sensores mecano-transcripcionales, delinear bucles de retroalimentación mecano-química y entender cómo fuerzas y genes cooperan para construir y mantener los tejidos vivos.
Sin duda, estamos ante un avance que redefine el estudio de la morfogénesis y la regulación génica. La mecano-transcriptómica espacial no es solo una técnica; es una nueva forma de mirar la biología.
Referencia
[1] Hallou A, He R, Simons BD, Dumitrascu B. A computational pipeline for spatial mechano-transcriptomics. Nat Methods. 2025 Mar 17. doi: 10.1038/s41592-025-02618-1.
AI bacterias Biología Sintética CRISPR cáncer envejecimiento Escherichia coli evolución Microbioma microbiota regulación resistencia salud VIH virus
Ultimos Productos
-
Curso de Organismos Modelo en Biología Molecular Febrero 2025
El precio original era: $75.00.$57.00El precio actual es: $57.00. -
Masterclass: Dinámica y Composición de los Condensados Biomoleculares
El precio original era: $80.00.$60.00El precio actual es: $60.00.
Buscar
Últimos Posts
Últimos Comentarios
Categorías
Archivos
- marzo 2026 (5)
- febrero 2026 (15)
- enero 2026 (21)
- diciembre 2025 (20)
- noviembre 2025 (16)
- octubre 2025 (21)
- septiembre 2025 (17)
- agosto 2025 (17)
- julio 2025 (19)
- junio 2025 (24)
- mayo 2025 (26)
- abril 2025 (49)
- marzo 2025 (20)
- febrero 2025 (10)
- enero 2025 (7)
- diciembre 2024 (8)
- noviembre 2024 (23)
- octubre 2024 (7)
Palabras clave
Sígue las noticias
Te invitamos a registrar tus datos como tu correo electrónico para que puedas recibir las últimas noticias y anuncios de Biología Molecular México

By signing up, you agree to the our terms and our Privacy Policy agreement.