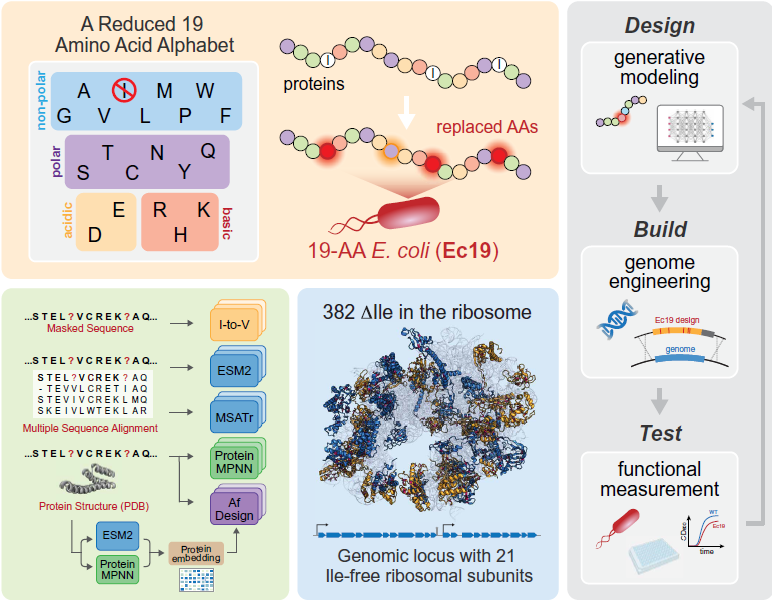
Todo ser vivo en la Tierra, desde las bacterias más simples hasta los humanos, utiliza el mismo conjunto universal de 20 aminoácidos canónicos para construir sus proteínas. Pero, ¿qué pasaría si pudiéramos simplificar este código fundacional? Un fascinante estudio publicado en la revista Science acaba de dar un paso monumental hacia la creación del primer organismo vivo con un alfabeto reducido a 19 aminoácidos, marcando un hito evolutivo sin precedentes desde la época del Último Ancestro Común Universal (LUCA).

El candidato perfecto para la eliminación Para lograr este desafío extremo de biología sintética, los científicos seleccionaron a la bacteria modelo Escherichia coli y se propusieron erradicar por completo la isoleucina (Ile) de sus proteínas esenciales. Los análisis evolutivos revelaron que este aminoácido es uno de los menos conservados en la naturaleza y comparte una gran similitud estructural y bioquímica con la valina y la leucina. Sin embargo, el camino no fue sencillo: al intentar sustituir directamente la isoleucina por valina o leucina en 39 proteínas esenciales de E. coli, solo el 43% de las variantes logró ser funcional en vivo. Una sustitución global simple demostró ser insuficiente para sostener la vida.
La IA generativa entra al rescate molecular Ante el fracaso de las sustituciones simples, los investigadores recurrieron al poder de la Inteligencia Artificial generativa. Utilizaron avanzados modelos de lenguaje de proteínas (como ESM2 y MSA Transformer) que aprenden las “reglas gramaticales” de la evolución, combinados con modelos predictivos basados en estructuras tridimensionales (como ProteinMPNN y AlphaFold2). Al enmascarar las posiciones de isoleucina, estas IA lograron diseñar secuencias completamente nuevas, proponiendo complejas mutaciones compensatorias que estabilizaron las proteínas sin necesidad de usar el aminoácido eliminado. A menudo, la IA sugirió aminoácidos que desafiaban la lógica tradicional del diseño de proteínas, demostrando que algoritmos estructurales y evolutivos pueden encontrar soluciones que la propia evolución natural no había explorado.
¡GRACIAS POR LEER NUESTRAS NOTICIAS! ¿Nos invitas un cáfe? ☕
El colosal rediseño del ribosoma bacteriano Para poner a prueba su método, el equipo apuntó a la maquinaria celular más compleja, esencial y conservada: el ribosoma. Este gigante molecular en E. coli está compuesto por 52 proteínas esenciales que albergaban un total de 382 residuos de isoleucina. A través de un riguroso marco de diseño, construcción y prueba, la IA logró generar variantes viables y libres de isoleucina para cada una de estas 52 subunidades, manteniendo una aptitud biológica superior al 90% en comparación con las proteínas naturales originales.
El clímax biotecnológico del experimento llegó cuando los científicos lograron agrupar 21 de estas subunidades ribosomales sintéticas en un único locus genómico nativo, creando una cepa viable bautizada como Ec19. Asombrosamente, esta célula de “alfabeto reducido” demostró ser evolutivamente robusta: al cultivarla ininterrumpidamente durante más de 450 generaciones en el laboratorio, la bacteria se mantuvo genómicamente estable y no mostró ninguna mutación de reversión para intentar recuperar la isoleucina.

Este trabajo pionero demuestra de manera contundente que es posible desafiar los bloques de construcción dictados por la naturaleza biológica moderna. Al fusionar la genómica de precisión con los modelos generativos de inteligencia artificial, la ciencia ha creado un mapa fundacional no solo para entender cómo evolucionó la vida primitiva con códigos genéticos más simples, sino para allanar el camino hacia el diseño de genomas sintéticos con alfabetos modificados y propiedades nunca antes vistas en el mundo natural.
——————————————————————————–
Referencia
Liu, L., Rochereau, C., Kozlov, S., Urtecho, G., et al. (2026). Toward life with a 19–amino acid alphabet through generative artificial intelligence design. Science. https://doi.org/10.1126/science.aeb5171













Deja una respuesta