📝 RESUMEN
Dentro de las células, el ARN no flota al azar; se organiza en grupos específicos llamados clústeres homotípicos, donde moléculas del mismo tipo se agrupan entre sí, ignorando a las demás. Un estudio biofísico revolucionario publicado en PNAS ha descifrado el mecanismo detrás de este reconocimiento: los palíndromos genéticos. Mediante simulaciones computacionales y análisis de secuencias en embriones de Drosophila, los investigadores descubrieron que las regiones palindrómicas permiten que dos hebras de ARN idénticas se unan de forma selectiva. Este hallazgo resuelve el misterio de cómo el ARN distingue lo “propio” de lo “ajeno” y revela una presión evolutiva para mantener estos palíndromos en genes críticos para el desarrollo.

1. El Enigma de la Identidad Molecular 🧩🦠
¡GRACIAS POR LEER NUESTRAS NOTICIAS! ¿Nos invitas un cáfe? ☕
Imagina una fiesta llena de gente donde todos llevan la misma ropa, pero solo deben agruparse con quienes tienen exactamente el mismo nombre. En el citoplasma celular ocurre algo similar: los ARNm de genes como nanos o pgc se agrupan únicamente con sus copias idénticas.
Hasta ahora, se pensaba que las interacciones ARN-ARN eran demasiado complejas como para permitir este nivel de discriminación, ya que cualquier secuencia puede, en teoría, pegarse parcialmente a otra. El problema es que el ARN tiende a plegarse sobre sí mismo (interacción intramolecular), lo que suele impedir la unión con otras moléculas.

2. La Magia de los Palíndromos: “Reconocerse en el Espejo” 🪞🧬
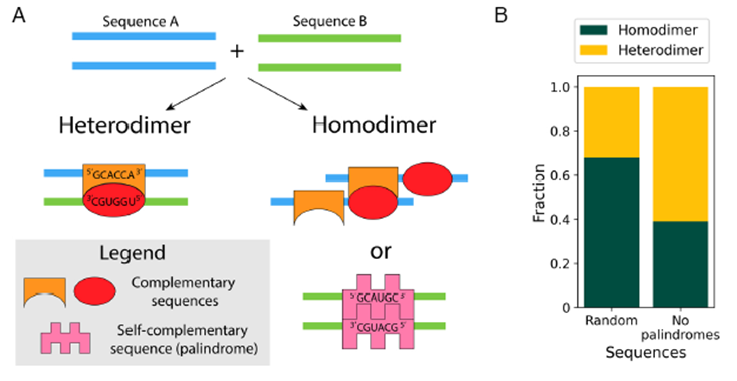
El equipo de investigación descubrió que la solución está en los palíndromos (secuencias que se leen igual al derecho y al revés, como “ANNA”). En el ARN, una secuencia palindrómica tiene una propiedad única: es complementaria a sí misma.
- El mecanismo: Cuando dos moléculas de ARN con el mismo palíndromo se encuentran, pueden formar un “puente” de pares de bases perfecto.
- La ventaja: A diferencia de las secuencias no palindrómicas, los palíndromos permiten una unión intermolecular que compite eficazmente con el plegamiento interno de la propia molécula. Esto crea un “pegamento” específico que solo funciona entre gemelos moleculares.
3. Evidencia en la Naturaleza: El caso de Drosophila 🦟🧫
Para validar esta hipótesis, los científicos analizaron los ARNm presentes en los gránulos germinales de moscas de la fruta. Encontraron que los genes que forman clústeres más fuertes, como nanos, presentan una densidad de palíndromos significativamente mayor que la que prediría el azar.
Incluso descubrieron que la evolución parece “proteger” estos palíndromos; aunque las secuencias cambien entre especies, la estructura palíndromica se conserva para asegurar que el ARN pueda seguir agrupándose correctamente durante el desarrollo del embrión.

4. Perspectivas: Lo Positivo y las Limitaciones del Descubrimiento ⚖️🔭
Lo Positivo e Impresionante:
- Simplicidad Elegante: Explica un fenómeno biológico complejo (la organización espacial de la célula) mediante reglas físicas básicas de apareamiento de bases.
- Potencial Biotecnológico: Este conocimiento permitiría diseñar “ARNs programables” que se agrupen solos en lugares específicos de la célula, lo que podría revolucionar las terapias de ARN mensajero o la creación de condensados artificiales para procesar señales biológicas.
Las Limitaciones que Debemos Tener en Cuenta:
- Modelo in silico: Gran parte de las conclusiones se basa en potentes simulaciones computacionales. Aunque los datos en moscas coinciden, se necesita validación experimental directa (crear mutantes sin palíndromos y comprobar si el clúster se deshace) para confirmar que no hay otros factores involucrados.
- Competencia de Proteínas: En la célula real, el ARN no está desnudo; está cubierto de proteínas que podrían ayudar o estorbar este reconocimiento por palíndromos. El siguiente paso es entender cómo las proteínas interactúan con este “código de espejos”.
📚 REFERENCIA BIBLIOGRÁFICA
Kimchi, O., Mitchel, K., Pyo, A. G. T., Wingreen, N. S., & Gavis, E. R. (2026). How do RNA molecules distinguish self from non-self? Proceedings of the National Academy of Sciences (PNAS), 123(15), e2602091123. https://doi.org/10.1073/pnas.2602091123













Deja una respuesta