📝 RESUMEN
Un consorcio internacional de científicos ha publicado en Nature un esfuerzo monumental para expandir el proteoma humano, identificando miles de nuevos marcos de lectura abiertos no canónicos (ncORFs). Mediante la integración de datos de Ribo-seq, espectrometría de masas y modelado estructural con AlphaFold, los investigadores han catalogado más de 7,000 nuevos productos de traducción. El estudio introduce los conceptos de microproteínas y peptideínas, clasificándolos en un sistema de tres niveles (Tiers) según la solidez de la evidencia, lo que redefine nuestra comprensión de la complejidad genómica y abre nuevas rutas para entender enfermedades y diseñar terapias.

1. Más allá de los genes conocidos: El universo ncORF 🌌🔬
¡GRACIAS POR LEER NUESTRAS NOTICIAS! ¿Nos invitas un cáfe? ☕
Durante décadas, pensamos que el genoma humano tenía unos 20,000 genes codificantes de proteínas “canónicos”. Sin embargo, este estudio demuestra que existen miles de regiones del genoma que antes considerábamos “no codificantes” pero que en realidad se traducen en péptidos funcionales.
- ncORFs: Estos marcos de lectura se encuentran en RNAs mensajeros (uORFs), RNAs supuestamente no codificantes (lncRNAs) o incluso en marcos de lectura alternativos de genes conocidos.

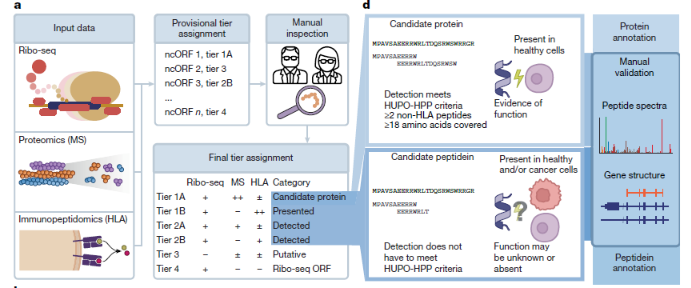
2. Metodología: La Triple Validación 🛠️📊
Para que una de estas microproteínas fuera aceptada, el equipo utilizó una combinación de tecnologías de vanguardia:
- Ribo-seq (Perfilado de Ribosomas): Para confirmar que los ribosomas realmente se están uniendo a esos fragmentos de RNA y traduciéndolos.
- Espectrometría de Masas (MS): Para detectar físicamente la presencia de los péptidos en las células.
- AlphaFold y Modelado Estructural: Se utilizó IA para predecir si estas nuevas secuencias pueden plegarse en estructuras estables o si corresponden a péptidos más cortos y flexibles.

3. Microproteínas vs. Peptideínas: ¿Cuál es la diferencia? 📏🧬
El estudio propone una nueva nomenclatura basada en la longitud y la estructura:
- Microproteínas (≥45 aminoácidos): Suelen tener estructuras plegadas más complejas y una mayor probabilidad de tener funciones bioquímicas tradicionales.
- Peptideínas (<45 aminoácidos): Son péptidos muy cortos que a menudo funcionan como señales celulares, moduladores de otras proteínas o componentes de complejos moleculares más grandes.

4. El Sistema de Tiers: Separando el Trigo de la Paja ⚖️🏷️
Debido a la gran cantidad de datos, los autores establecieron una jerarquía de confianza:
- Tier 1 (Alta Confianza): Proteínas con evidencia contundente de traducción y detección física por MS.
- Tier 2 (Confianza Media): Evidencia sólida de traducción (Ribo-seq) pero con detección limitada o nula por espectrometría de masas todavía.
- Tier 3 (Candidatos): Regiones con potencial de traducción según el análisis bioinformático pero que requieren más validación experimental.
5. ¿Por qué es esto importante para el futuro? 🚀🩺
Este “atlas” expandido del proteoma humano tiene implicaciones masivas:

- Nuevos Biomarcadores: Muchas de estas microproteínas podrían ser marcadores específicos de cáncer o enfermedades neurodegenerativas.
- Evolución del Genoma: Ayuda a entender cómo surgen nuevos genes (genes de novo) a partir de secuencias que antes no tenían función.
- Actualización de Bases de Datos: Instituciones como UniProt y GENCODE ahora tienen una referencia estandarizada para incluir estos miles de nuevos elementos.
📚 REFERENCIA BIBLIOGRÁFICA
Deutsch, E. W., Kok, L. W., Mudge, J. M., Valls, C. F., et al. (2026). Expanding the human proteome with microproteins and peptideins. Nature, 630, 1-15. https://doi.org/10.1038/s41586-026-10459-x
















Deja una respuesta