📝 RESUMEN
Aunque los científicos son expertos en leer el código de las proteínas (que representa solo el 2% del genoma), el 98% restante del genoma, el genoma regulador, sigue siendo un enigma lingüístico. Este artículo narra un editorial de Nature que detalla cómo los Massively Parallel Reporter Assays (MPRAs) permiten a los investigadores medir simultáneamente millones de variantes genéticas para entender cómo los promotores y potenciadores (enhancers) regulan la expresión génica. Gracias a la combinación de estas herramientas moleculares y la Inteligencia Artificial, la ciencia está pasando de simplemente “leer” el genoma a tener la capacidad de “escribir” y diseñar circuitos genéticos de alta precisión para medicina y biotecnología.
1. El Desafío del “Lado Oscuro” del Genoma 🌑🧬
¡GRACIAS POR LEER NUESTRAS NOTICIAS! ¿Nos invitas un cáfe? ☕
Cada vez que secuenciamos a un individuo, encontramos millones de variantes, pero solo el 0.6% ocurre en regiones que codifican proteínas.
- El vacío de conocimiento: “Realmente no entendemos qué está haciendo el resto; no tenemos un código regulador”, señala el genetista Nadav Ahituv.
- Los interruptores: El reto es identificar qué secuencias actúan como promotores (iniciadores) y cuáles como potenciadores (controles de volumen) en tejidos específicos.
2. MPRAs: El Acelerador de Partículas de la Genética 🚀🔬
Para no perderse en la inmensidad del genoma, los científicos usan los MPRAs, que reducen la complejidad a sistemas sintéticos controlados.
- Funcionamiento: Se crean bibliotecas de millones de fragmentos de ADN, cada uno unido a un “código de barras” único.
- Medición masiva: Al introducir estos fragmentos en células, se puede secuenciar el ARN producido y usar los códigos de barras para saber exactamente qué variante aumentó o disminuyó la expresión del gen.
- Evolución técnica: Desde los primeros ensayos en 2009 en tubos de ensayo, hoy los MPRAs se realizan en células cultivadas e incluso se integran directamente en el genoma mediante tecnologías como CRISPR para mayor realismo biológico.

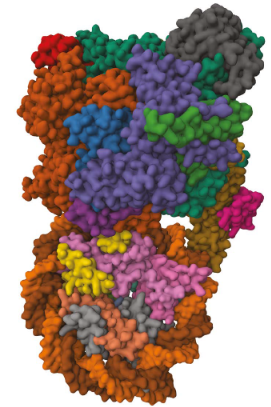
La imagen muestra cómo los reguladores (mostrados en café y naranja) se envuelven en proteínas, demostrando la complejidad de entender la “gramática” de la regulación genética.
3. Inteligencia Artificial: El Traductor Universal 🤖🧠
El volumen de datos generado por los MPRAs es tan masivo que la IA se ha vuelto indispensable.
- Entrenamiento de modelos: Los datos de estos ensayos sirven para entrenar sistemas de IA capaces de predecir cómo afectará una mutación a la salud de una persona sin necesidad de experimentos físicos previos.
- Diseño de novo: La meta final no es solo entender el código natural, sino diseñar elementos reguladores artificiales que activen terapias génicas únicamente en el tejido enfermo (por ejemplo, solo en células tumorales), evitando efectos secundarios en el resto del cuerpo.
4. Perspectivas y Horizontes 🌍✨
Lo Positivo e Impresionante:
- Medicina de precisión: Esta tecnología permitirá interpretar los 3.5 millones de variantes que tiene cada humano y saber cuáles son realmente peligrosas.
- Bioingeniería: La capacidad de diseñar “perillas” de control genético abre puertas no solo en salud, sino en agricultura y biotecnología industrial.
El “Wildcard” (Dato Curioso/Extra):
- Aunque la medicina es el enfoque principal, estas herramientas podrían usarse para entender cómo cambios minúsculos en el ADN regulador permitieron a los humanos desarrollar cerebros más grandes o caminar erguidos en comparación con otros primates.
📚 REFERENCIAS CITADAS EN EL ARTÍCULO.
- Patwardhan, R. et al. Nature Biotechnol. 27, 1173–1175 (2009).
- Arnold, C. D. et al. Science 339, 1074–1077 (2013).
- Agarwal, V. et al. Nature 639, 411–420 (2025).
- Martinez-Ara, M., Comoglio, F., van Arensbergen, J. & van Steensel, B. Mol. Cell 82, 2519–2531 (2022).
- Arnould, C. et al. Preprint at bioRxiv https://doi.org/10.1101/2025.06.11.658967 (2025).
- Kreimer, A. et al. Nature Commun. 13, 1504 (2022).
- Lee, S. et al. Cell 188, 1409–1424 (2025).
- Weiss, C. V. et al. eLife 10, e63713 (2021).
- Barbadilla-Martínez, L. et al. Nature 651, 1107–1116 (2026).
- Gosai, S. J. et al. Nature 634, 1211–1220 (2024).














Deja una respuesta