Resumen
Un estudio reciente, publicado en Cell Reports por Keshet y Benvenisty, utiliza la tecnología Perturb-seq (CRISPR de célula única) para mapear la intrincada red de regulación génica (GRN) que sustenta la pluripotencia en células madre pluripotentes humanas (hPSCs). La investigación revela cómo factores de transcripción (TFs) específicos actúan como “guardianes” que bloquean la diferenciación hacia linajes particulares y cómo esta red se reconfigura drásticamente entre los estados naive (preimplantación) y primed (postimplantación). Además, se descubre que esta red regula la expresión de elementos transponibles, lo que sugiere un papel evolutivo clave en la identidad celular.

1. El Desafío de la Pluripotencia Humana 🧬
¡GRACIAS POR LEER NUESTRAS NOTICIAS! ¿Nos invitas un cáfe?
Aunque se conocen los factores nucleares “maestros” (OCT4, SOX2, NANOG), la arquitectura completa de la red que permite a las hPSCs autorrenovarse o diferenciarse ha sido difícil de definir. Gran parte del conocimiento actual proviene de ratones, pero la pluripotencia humana es distinta y presenta dos estados clave:
- Naive: Similar al epiblasto previo a la implantación.
- Primed: Similar al epiblasto posimplantación, listo para diferenciarse.
2. Metodología: Perturb-seq 🔬
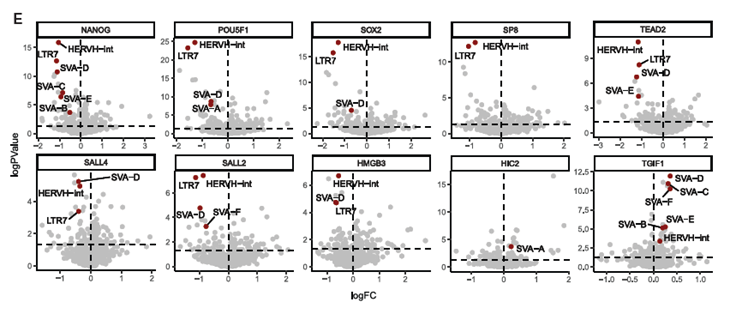
Los autores seleccionaron 41 factores de transcripción esenciales para el crecimiento de las hPSCs y altamente expresados en ellas. Utilizando CRISPR acoplado a la secuenciación de ARN de célula única, pudieron observar el efecto individual de silenciar cada gen en miles de células simultáneamente.
3. Hallazgos Principales: Guardianes y Atenuadores 🛡️
La red no es una simple jerarquía, sino un sistema complejo de retroalimentación:
- Guardianes de Linaje: Ciertos TFs bloquean específicamente la salida hacia linajes como el neuroectodermo o el mesendodermo. Por ejemplo, el KO de POU5F1 provoca una diferenciación masiva, mientras que NANOG previene específicamente la diferenciación neural.
- Atenuadores de Pluripotencia: Se identificaron factores, como SMARCC1 y TGIF1, que normalmente “frenan” la pluripotencia para mantener a la célula sensible a las señales de diferenciación.
- Control de Elementos Transponibles (TEs): La red regula activamente “genes saltarines” como HERVH/LTR7, que son fundamentales para la identidad de las células madre humanas.

4. Comparativa: Estado Naive vs. Primed 🌓
Al replicar el experimento en células en estado naive, se observaron cambios fascinantes:
- Diferenciación por Defecto: En el estado naive, la pérdida de la mayoría de los TFs esenciales conduce casi exclusivamente a la formación de trofoblasto (tejido de la placenta), a diferencia del estado primed donde se generan las tres capas germinales.
- Reconfiguración de la Red: TFs como HMGB3 y SP8 resultaron ser críticos para el estado naive pero prescindibles en el primed.

| Característica | hPSCs Primed | hPSCs Naive |
| Linaje tras KO de TFs | Multilinaje (Ecto/Meso/Endo) | Principalmente Trofectodermo |
| Factores Clave Únicos | SMARCC1 | SP8, HMGB3 |
| Regulación de TEs | Activación de ERV1 / Inhibición L1 | Activación SVA y Alu |
Bibliografía
- Keshet, G., & Benvenisty, N. (2026). A single-cell CRISPR screen defines a gene regulatory network governing human pluripotency in primed and naive cells. Cell Reports, 45(117124). https://doi.org/10.1016/j.celrep.2026.117124.













Deja una respuesta