Un equipo internacional desarrolló BindCraft, una plataforma computacional que permite diseñar proteínas enlazadoras desde cero en un solo intento. A diferencia de los métodos tradicionales, que requieren largos procesos de cribado experimental, BindCraft se basa en AlphaFold2 y algoritmos de inteligencia artificial para generar proteínas con afinidades en el rango nanomolar, listas para aplicaciones terapéuticas y biotecnológicas.
En pocas palabras
- Qué es: BindCraft, una plataforma abierta para diseñar proteínas enlazadoras de novo.
- Cómo funciona: combina AlphaFold2, optimización de secuencias y filtros estructurales.
- Ventaja clave: elimina la necesidad de cribado experimental masivo.
- Resultados: enlazadores efectivos contra receptores inmunológicos, alergenos, nucleasas y virus terapéuticos.
- Impacto: abre la puerta a terapias personalizadas, nuevos fármacos y herramientas biotecnológicas.

Una nueva herramienta para diseñar proteínas
¡GRACIAS POR LEER NUESTRAS NOTICIAS! ¿Nos invitas un cáfe? ☕
Las proteínas rara vez trabajan solas; dependen de interacciones específicas para regular procesos biológicos. Manipular estas interacciones —por ejemplo, bloqueando receptores, neutralizando toxinas o redirigiendo virus terapéuticos— abre enormes posibilidades en medicina y biotecnología.
Tradicionalmente, generar proteínas enlazadoras requería estrategias como la inmunización de animales, bibliotecas de anticuerpos o evolución dirigida. Estos métodos son costosos, lentos y con poca capacidad de controlar el sitio exacto de unión.
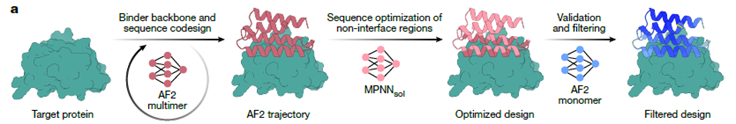
BindCraft cambia este paradigma: automatiza todo el diseño, reduciendo la intervención humana y democratizando la creación de enlazadores. Su mayor innovación es que “imagina” nuevas proteínas optimizadas directamente en la computadora, evitando el cribado de miles de candidatos.
Cómo funciona BindCraft
- Predicción inicial: utiliza AlphaFold2 multimer para modelar complejos proteína–proteína desde cero.
- Optimización: ajusta secuencias y estabilidad con MPNNsol, preservando la zona de unión.
- Filtrado final: aplica predicciones adicionales y análisis físico-químicos para descartar modelos poco realistas.
Así, cualquier laboratorio puede generar candidatos funcionales listos para sintetizar y probar, sin ser experto en bioinformática.
Resultados destacados
Los autores pusieron a prueba BindCraft en 12 blancos distintos, muchos de ellos de alto interés biomédico:
- Receptores inmunológicos (PD-1, PD-L1, IFNAR2, CD45): obtuvieron enlazadores con afinidades nanomolares, comparables a anticuerpos terapéuticos.
- Alergenos comunes (Der f7, Der f21, Bet v1): diseñaron proteínas capaces de bloquear la unión de IgE en suero de pacientes alérgicos, reduciendo reacciones potenciales.
- CRISPR-Cas9 y Argonautas bacterianos: crearon inhibidores artificiales de nucleasas, abriendo nuevas posibilidades para modular la edición génica.
- Proteínas de novo: incluso sin información previa, lograron enlazadores funcionales, validando la flexibilidad del método.
- Vectores virales (AAV): al integrar los enlazadores en cápsides virales, reprogramaron su tropismo celular, un avance clave para terapias génicas dirigidas.

Implicaciones
BindCraft alcanza tasas de éxito experimental de 10 a 100%, con un promedio de 46%, lo cual es excepcional para un método totalmente computacional. Aunque persisten limitaciones (alto costo computacional y posibles problemas de inmunogenicidad en aplicaciones clínicas), representa un paso enorme hacia el ideal de “un diseño, un enlazador”.
Esto significa que en el futuro cercano será posible generar proteínas a la carta para terapias personalizadas, diagnóstico de enfermedades o biotecnología industrial.
Referencia:
Pacesa, M., Nickel, L., Schellhaas, C., Schmidt, J., Pyatova, E., Kissling, L., et al. (2025). One-shot design of functional protein binders with BindCraft. Nature. https://doi.org/10.1038/s41586-025-09429-6