En Pocas Palabras:
Las enzimas son los catalizadores de la vida, acelerando las reacciones químicas con una eficiencia y selectividad asombrosas. Durante décadas, los científicos han soñado con diseñar enzimas artificiales “de novo” (desde cero) para realizar reacciones nuevas o mejorar las existentes, pero las enzimas diseñadas por computadora solían ser muy poco eficientes en comparación con sus contrapartes naturales, requiriendo mucha optimización experimental. Ahora, un equipo de investigadores ha logrado un avance monumental: utilizando un flujo de trabajo completamente computacional, han diseñado nuevas enzimas para una reacción modelo (la eliminación de Kemp) que son tan rápidas y eficientes como las enzimas naturales promedio, e incluso superan a diseños computacionales previos en dos órdenes de magnitud. Este logro no solo supera una limitación importante en el diseño de enzimas, sino que también desafía algunas suposiciones fundamentales sobre la biocatálisis y abre la puerta a la programación de enzimas de alta eficiencia con un esfuerzo experimental mínimo.

El Santo Grial del Diseño de Enzimas
Las enzimas son las maravillas moleculares de la naturaleza. Estas proteínas actúan como catalizadores biológicos increíblemente potentes y específicos, acelerando las reacciones químicas esenciales para la vida en órdenes de magnitud. La capacidad de diseñar enzimas a medida para realizar reacciones específicas, especialmente aquellas que no ocurren en la naturaleza, ha sido un objetivo largamente anhelado en la biología sintética y la biotecnología. Sin embargo, a pesar de los avances en el diseño computacional de proteínas, las enzimas creadas “de novo” (desde cero, sin recurrir a una enzima natural que ya realice esa reacción) han demostrado consistentemente una eficiencia catalítica muy inferior a la de las enzimas naturales, requiriendo a menudo laboriosos y extensos ciclos de optimización experimental (evolución dirigida en el laboratorio) para alcanzar niveles de actividad útiles. Este “abismo catalítico” ha expuesto lagunas críticas en nuestra comprensión de los fundamentos de la biocatálisis. Un nuevo y revolucionario estudio publicado en la prestigiosa revista Nature por Dina Listov, Sarel J. Fleishman y un equipo internacional de colaboradores, marca un hito al presentar un flujo de trabajo completamente computacional capaz de diseñar enzimas artificiales de alta eficiencia, con parámetros catalíticos comparables a los de las enzimas naturales, y todo ello con un esfuerzo experimental mínimo.
El Desafío de la Eliminación de Kemp: Un Modelo para el Diseño de Novo
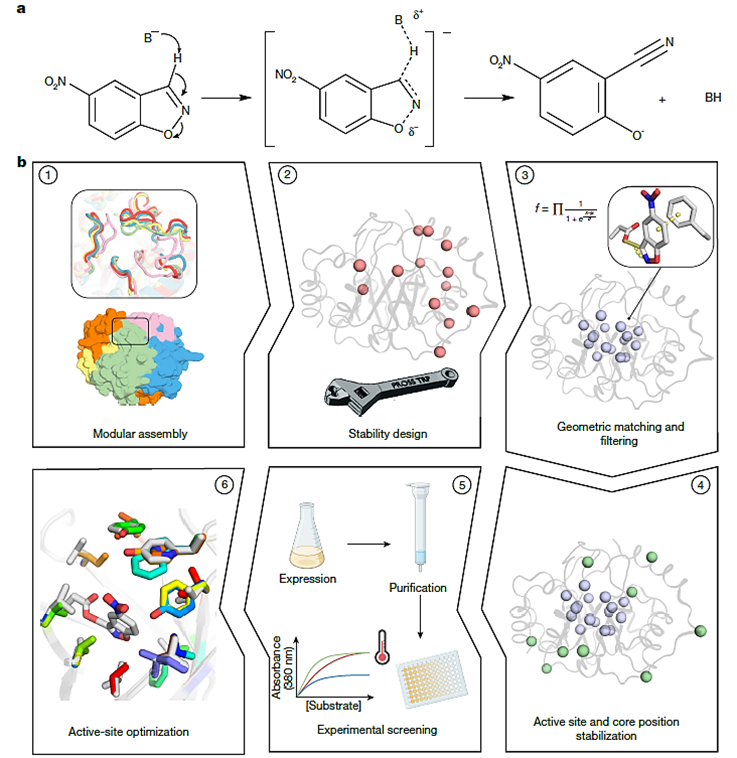
Para probar su nueva estrategia de diseño, el equipo se centró en la reacción de eliminación de Kemp, una reacción modelo clásica para la abstracción de protones catalizada por una base, que ha servido durante mucho tiempo como campo de pruebas para el diseño de enzimas de novo, precisamente porque no se conoce ninguna enzima natural que la catalice. A pesar de la sofisticación creciente en los métodos de diseño, las “eliminasa de Kemp” diseñadas computacionalmente hasta la fecha eran notablemente ineficientes.
Una Nueva Estrategia Computacional: Estabilidad, Plegabilidad y Actividad Precisa
La hipótesis de trabajo de los investigadores fue que el diseño enzimático efectivo requiere un control exquisito sobre todos los grados de libertad de la proteína para asegurar no solo la estabilidad y la plegabilidad (la capacidad de la proteína para adoptar de forma única la estructura tridimensional diseñada), sino también el posicionamiento preciso de los grupos catalíticos en el sitio activo y la interacción óptima con el estado de transición de la reacción (el “teozima”).
Su flujo de trabajo computacional, aplicado a la versátil estructura de barril TIM (una de las arquitecturas proteicas más comunes en las enzimas naturales), implicó varios pasos clave:
- Generación de Diversidad de Andamios (Backbones): En lugar de partir de un único andamio, utilizaron un ensamblaje combinatorio de fragmentos de proteínas naturales para generar miles de nuevas estructuras de barril TIM, introduciendo diversidad estructural.
- Estabilización Global: Aplicaron métodos computacionales (como PROSS) para estabilizar la conformación general de estos andamios diseñados.
- Diseño del Sitio Activo: Utilizaron algoritmos de “emparejamiento geométrico” para posicionar los residuos catalíticos clave (el teozima para la eliminación de Kemp) dentro de los andamios, y luego optimizaron el resto del sitio activo mediante cálculos atomísticos detallados para favorecer la catálisis.
- Estabilización del Núcleo y Sitio Activo: Finalmente, aplicaron refinamientos adicionales para estabilizar el sitio activo y el núcleo de la proteína.

Resultados Espectaculares: Enzimas Artificiales con Eficiencia Natural
De los varios diseños probados experimentalmente, varios mostraron actividad. Uno de ellos, Des27.7, que presentaba más de 140 mutaciones respecto a cualquier proteína natural conocida, exhibió resultados notables:
- Alta Estabilidad: Era muy estable, resistiendo temperaturas superiores a 85 °C.
- Eficiencia Catalítica Impresionante: Mostró una eficiencia catalítica (kcat/KM) de 12,700 M⁻¹s⁻¹ y una tasa de recambio (kcat) de 2.8 s⁻¹. Esto representa una mejora de dos órdenes de magnitud (unas 100 veces) sobre los mejores diseños computacionales previos para esta reacción.
- Superando Suposiciones: Sorprendentemente, al modificar un residuo que se consideraba esencial en todos los diseños previos de eliminasa de Kemp (un residuo aromático para interacciones de apilamiento-π con el sustrato) por un residuo alifático (leucina), la eficiencia de Des27.7 aumentó espectacularmente a más de 10⁵ M⁻¹s⁻¹ y la tasa a 30 s⁻¹. Estos valores son comparables a los de las enzimas naturales promedio y desafían suposiciones fundamentales sobre los requisitos para la catálisis de esta reacción.

Los análisis estructurales y de dinámica molecular sugirieron que el éxito de Des27.7 se debe a una mejor preorganización del sitio activo, una mayor afinidad por el sustrato y la capacidad de adoptar múltiples conformaciones productivas.
Implicaciones del Avance:
Este logro tiene implicaciones profundas y de gran alcance:
- Validación del Diseño Computacional Atomístico: Demuestra que los métodos computacionales actuales, cuando se aplican de manera integral y considerando múltiples aspectos del diseño proteico, son capaces de generar enzimas de novo con alta eficiencia sin necesidad de extensas campañas de evolución dirigida en laboratorio.
- Programación de la Biocatálisis: Nos acerca un paso más a la capacidad de “programar” enzimas a la carta para catalizar virtualmente cualquier reacción química deseada, con enormes aplicaciones en la industria química, farmacéutica, la biorremediación y la producción de biocombustibles.
- Comprensión Fundamental de las Enzimas: El éxito y los fracasos en el diseño de novo proporcionan información invaluable sobre los principios fundamentales que gobiernan la catálisis enzimática, la estabilidad de las proteínas y la relación estructura-función. El hallazgo de que un sitio activo completamente alifático puede ser tan eficiente desafía dogmas establecidos.
- Democratización del Diseño de Enzimas: Un flujo de trabajo computacional robusto y eficiente podría hacer que el diseño de enzimas sea accesible a un mayor número de investigadores, acelerando la innovación.
Conclusión: Una Nueva Era para las Enzimas Diseñadas
El trabajo de Listov, Fleishman y su equipo representa un avance paradigmático en el campo del diseño de enzimas. Al superar la barrera de la baja eficiencia que había plagado a las enzimas diseñadas de novo, han demostrado el poder de los enfoques computacionales integrales y han abierto una nueva era de posibilidades para la ingeniería de proteínas y la biocatálisis. Este hito no solo nos proporciona herramientas más poderosas para crear los catalizadores del futuro, sino que también profundiza nuestra comprensión de los principios fundamentales que rigen la maquinaria molecular de la vida.
Referencia del Artículo:
Listov, D., Vos, E., Hoffka, G., Hoch, S. Y., Bergs, A., Hamer-Rogotner, S., … & Fleishman, S. J. (2025). Complete computational design of high-efficiency Kemp elimination enzymes. Nature. https://doi.org/10.1038/s41586-025-09136-2
(Publicado online; la paginación final puede variar).