¡Tu carrito está actualmente vacío!
LEGO para Células: Crean un “Kit de Herramientas” para Programar Levaduras y Construir Organismos Multicelulares a la Carta
Introducción: El Salto a la Multicelularidad, Ahora en el Laboratorio
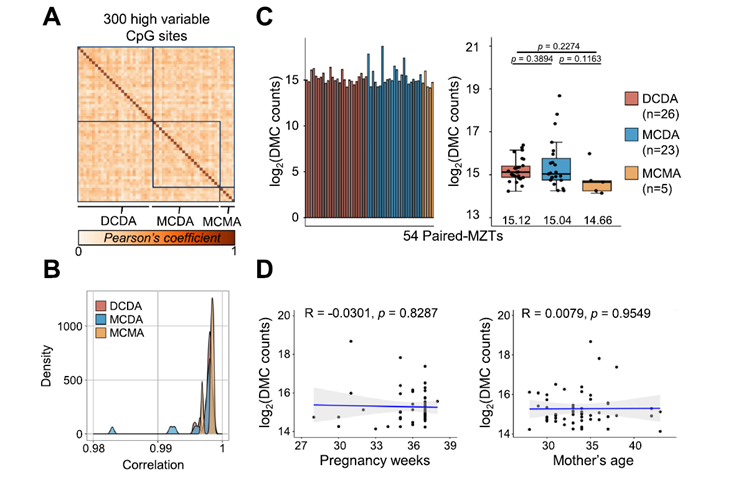
La transición de la vida unicelular a la multicelularidad, que ocurrió hace cientos de millones de años, fue uno de los eventos más transformadores en la historia de nuestro planeta. Permitió la evolución de organismos complejos como las plantas y los animales, gracias al desarrollo de dos capacidades fundamentales: la adhesión celular selectiva (la habilidad de las células para “pegarse” a otras específicas) y la comunicación por contacto (la habilidad de las células de enviarse señales solo cuando se tocan). Ahora, un equipo de investigadores del Imperial College London, liderado por Fankang Meng y Tom Ellis, ha dado un paso gigantesco en la recreación de este proceso en el laboratorio. En un artículo publicado en la prestigiosa revista Cell, presentan una serie de “kits de herramientas” genéticas que permiten programar a la levadura de panadero (Saccharomyces cerevisiae), un organismo típicamente unicelular, para que exhiba comportamientos multicelulares complejos, desde formar patrones y circuitos lógicos hasta detectar interacciones entre proteínas.
Los Kits de Herramientas: MARS, SATURN y JUPITER
El equipo desarrolló un conjunto de tres sistemas modulares y programables, nombrados en honor a los gigantes del sistema solar, que dotan a la levadura de capacidades que no posee de forma natural:

- SATURN (Saccharomyces Adhesion Toolkit for mUlticellular patteRNing): Este es el “pegamento” programable. Utiliza pares de proteínas de alta afinidad (como antígeno-nanocuerpo o dockerina-cohesina) que se expresan en la superficie de diferentes poblaciones de levaduras. Esto permite que las células se adhieran entre sí de manera altamente específica, como si fueran piezas de LEGO que solo encajan con su par correspondiente. Con SATURN, los investigadores pueden diseñar qué células se pegan a cuáles, creando patrones multicelulares predefinidos (como estructuras en forma de malla, fibrosas o esféricas) simplemente mezclando diferentes poblaciones celulares.
- MARS (Mating-peptide Anchored Response System): Este es el sistema de “comunicación por contacto”. Normalmente, la levadura se comunica a distancia liberando feromonas (péptidos de apareamiento) que se difunden. MARS modifica este sistema: en lugar de secretar el péptido, lo ancla a la superficie celular. Ahora, una célula “emisora” (con el péptido anclado) solo puede activar a una célula “receptora” (con el receptor correspondiente) si ambas entran en contacto físico directo. Esto imita la señalización yuxtacrina, un tipo de comunicación crucial en el desarrollo embrionario de los animales.
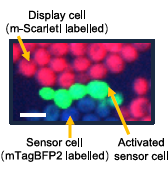
- JUPITER (JUxtacrine sensor for Protein-protein InTERaction): Este es el sistema más sofisticado, que combina la adhesión de SATURN con la señalización de MARS para crear un sensor genético de interacciones entre proteínas (PPIs). Funciona así: una célula “display” muestra una proteína de interés (por ejemplo, un antígeno) y un péptido MARS. Una célula “sensor” muestra una segunda proteína (un nanocuerpo) y el receptor MARS correspondiente. Solo si el antígeno y el nanocuerpo se unen con suficiente afinidad (manteniendo las células juntas), la señalización MARS se activa, produciendo una señal de fluorescencia. La intensidad de la señal es proporcional a la fuerza de la interacción.

Construyendo con Levadura: De Circuitos Lógicos a Cribado de Fármacos
La combinación de estas herramientas permite programar comportamientos multicelulares de una complejidad sin precedentes en levadura:
- Patrones de Desarrollo y Circuitos Lógicos: Al combinar MARS y SATURN, los investigadores crearon poblaciones de levaduras que se auto-organizan en patrones y luego, basándose en su posición y sus “vecinos”, activan la expresión de genes específicos. Construyeron el equivalente a circuitos lógicos multicelulares (OR, NOR, AND, XOR), donde la “respuesta” de una célula depende de la presencia de una, otra, ambas o ninguna de las células vecinas. Esto es análogo a cómo las células en un embrión se diferencian en diferentes tipos celulares según las señales que reciben de su entorno local.
- Aislamiento y Separación de Fases: Crearon poblaciones de tres tipos de células donde cada tipo solo se adhería a sí mismo, logrando una “separación de fases” similar a la que ocurre en el desarrollo de tejidos.
- Puentes Celulares: Diseñaron una célula “puente” que podía adherirse a otras dos que, de otro modo, no interactuarían, uniéndolas físicamente y permitiendo la comunicación entre ellas.
- Cribado de Alta Afinidad con JUPITER: Demostraron que JUPITER puede usarse como una poderosa herramienta de cribado. Pudieron identificar y enriquecer variantes de nanocuerpos con mayor afinidad por su antígeno a partir de una biblioteca, simplemente seleccionando las células que mostraban mayor fluorescencia o que podían crecer en un medio selectivo.

Implicaciones y Futuro de la Biología Sintética
Este trabajo no es solo un tour de force de la ingeniería genética; abre un abanico de posibilidades para la ciencia y la biotecnología:
- Entendiendo la Multicelularidad: Ofrece una plataforma sin precedentes para estudiar los principios fundamentales de la auto-organización y el desarrollo multicelular desde cero, permitiendo a los científicos “jugar” con las reglas de la adhesión y la comunicación.
- Ingeniería de Tejidos y Biomateriales: Podría sentar las bases para programar células de levadura o incluso de mamíferos para que se auto-ensamblen en estructuras 3D complejas o en biomateriales “vivos” con funciones programadas.
- Descubrimiento de Fármacos y Anticuerpos: JUPITER representa una nueva y potente plataforma para el cribado de interacciones proteína-proteína, lo que podría acelerar enormemente el descubrimiento de nuevos fármacos o la selección de anticuerpos terapéuticos (como los nanocuerpos) con alta afinidad.
- Biosensores y Computación Celular: La capacidad de construir circuitos lógicos multicelulares allana el camino para el diseño de “consorcios” microbianos inteligentes que puedan actuar como biosensores complejos o realizar tareas de computación biológica.
Conclusión: Programando la Vida en Comunidad
El trabajo de Meng, Ellis y su equipo ha dotado a la humilde levadura de un conjunto de superpoderes multicelulares. Al crear los toolkits MARS, SATURN y JUPITER, han proporcionado a la comunidad de biología sintética un conjunto de “piezas de LEGO” moleculares para construir y programar la adhesión celular y la comunicación por contacto con una precisión y modularidad sin precedentes. Esto no solo nos permite emular y entender los procesos que dieron origen a la vida compleja en nuestro planeta, sino que también expande drásticamente el alcance de lo que podemos construir con la biología, desde la creación de tejidos programados hasta el descubrimiento de la próxima generación de medicamentos.
Referencia del Artículo:
Meng, F., Shaw, W. M., Kam, Y. K. K., & Ellis, T. (2025). Engineering yeast multicellular behaviors via synthetic adhesion and contact signaling. Cell, 188, 1–14. https://doi.org/10.1016/j.cell.2025.06.025
AI bacterias Biología Sintética CRISPR cáncer envejecimiento Escherichia coli evolución Microbioma microbiota regulación resistencia salud VIH virus
Ultimos Productos
-
Curso de Organismos Modelo en Biología Molecular Febrero 2025
El precio original era: $75.00.$57.00El precio actual es: $57.00. -
Masterclass: Dinámica y Composición de los Condensados Biomoleculares
El precio original era: $80.00.$60.00El precio actual es: $60.00.
Buscar
Últimos Posts
Últimos Comentarios
Categorías
Archivos
- marzo 2026 (5)
- febrero 2026 (15)
- enero 2026 (21)
- diciembre 2025 (20)
- noviembre 2025 (16)
- octubre 2025 (21)
- septiembre 2025 (17)
- agosto 2025 (17)
- julio 2025 (19)
- junio 2025 (24)
- mayo 2025 (26)
- abril 2025 (49)
- marzo 2025 (20)
- febrero 2025 (10)
- enero 2025 (7)
- diciembre 2024 (8)
- noviembre 2024 (23)
- octubre 2024 (7)
Palabras clave
Sígue las noticias
Te invitamos a registrar tus datos como tu correo electrónico para que puedas recibir las últimas noticias y anuncios de Biología Molecular México

By signing up, you agree to the our terms and our Privacy Policy agreement.